Projets de Recherche
Sycomia développe des projets de recherche appliquée centrés sur la conception de pipelines bioinformatiques pour l’ADN tumoral circulant (ctDNA), à l’intersection entre la génomique et l'intelligence artificielle pour l’oncologie de précision.
Pipeline d’analyse de ctDNA multi-plateformes pour l’oncologie de précision
Le cancer reste l’un des défis majeurs de santé publique de notre époque. Bien que les thérapies continuent de progresser, le diagnostic et le suivi thérapeutique restent insuffisants : trop invasifs, trop tardifs et insuffisamment informatifs au niveau moléculaire. Les méthodes classiques, telles que la biopsie tumorale ou l’imagerie médicale, ne permettent pas d’identifier la maladie résiduelle minimale, c’est-à-dire la petite population de cellules tumorales survivantes qui annoncent une rechute imminente.
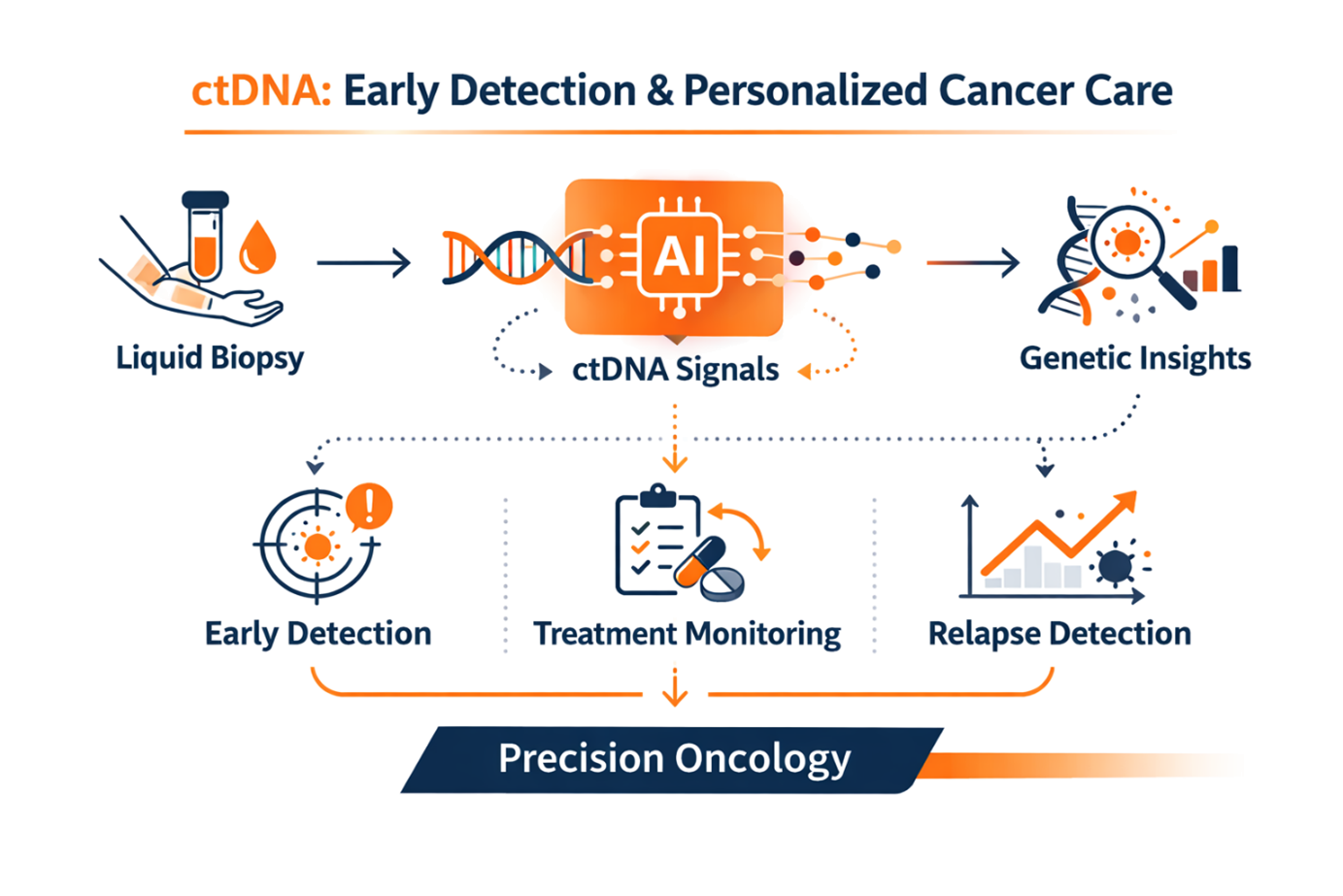
La biopsie liquide change la donne. En analysant les ctDNA à partir d’un simple prélèvement sanguin, il devient possible de détecter le cancer à un stade plus précoce, de suivre la réponse au traitement en temps réel et d’anticiper une rechute avant qu’elle ne devienne cliniquement apparente. Sycomia développe un pipeline bioinformatique multi-plateformes qui exploite pleinement le potentiel de cette technologie, en intégrant nativement les trois principales technologies de séquençage ainsi qu’une couche d’intelligence artificielle pour transformer les données brutes en résultats cliniquement exploitables.
Notre pipeline bioinformatique pour le ctDNA
Notre pipeline bioinformatique pour l'analyse de ctDNA intègre trois technologies de séquençage complémentaires : le séquençage à lectures courtes (Illumina) avec des identifiants moléculaires uniques pour la détection ultra-sensible des mutations ponctuelles, et le séquençage à lectures longues (Oxford Nanopore et PacBio HiFi) pour la détection directe des variants structurels, des fusions géniques et des réarrangements chromosomiques. Les technologies à lectures longues permettent également la lecture native des modifications épigénétiques telles que la méthylation de l’ADN, fournissant des informations génomiques et épigénomiques simultanément à partir des mêmes molécules, une capacité inaccessible aux approches actuelles utilisant une seule technologie.
L’intelligence artificielle est intégrée à chaque étape de l’analyse. Elle permet la fusion de signaux multimodaux, une meilleure discrimination signal/bruit dans des régions génomiques complexes, la classification des cancers avec une sensibilité accrue, la prédiction du tissu d’origine et l’évaluation de l’efficacité des traitements. Le résultat est un pipeline modulaire et containerisé, compatible avec plusieurs plateformes de séquençage, capable de fournir des rapports cliniques structurés en 48 à 72 heures.
Ce qui nous distingue
Les solutions actuelles de ctDNA sur le marché reposent exclusivement sur le séquençage à lectures courtes Illumina et sur des panels géniques propriétaires limités à quelques dizaines de cibles. Sycomia adopte une approche fondamentalement différente : indépendante de la plateforme, multi-technologies et ouverte à toutes les données de séquençage, quelle que soit leur origine.
Cette position nous permet de collaborer avec les laboratoires de séquençage existants plutôt que de rivaliser avec eux. Notre pipeline bioinformatique pour le ctDNA est conçu pour être ouvert à toutes les données de séquençage, quelle que soit leur origine, favorisant ainsi des partenariats à l’échelle de tout l’écosystème : hôpitaux, centres de recherche universitaires, CRO et entreprises de biotechnologie.
Sycomia est actuellement en phase de développement actif du pipeline, avec une feuille de route de six mois structurée en trois étapes : preuve de concept technique sur des jeux de données de référence publics, validation sur 20 à 30 échantillons pilotes, et intégration de modèles d’IA pour l’analyse multimodale et la génération automatisée de rapports.
Le pipeline vise une sensibilité de détection d’une fréquence allélique des variants (VAF) de 0,01 %, avec un taux de faux positifs inférieur à 0,1 % et un délai total de restitution des résultats de 48 à 72 heures.